
涂世隆 (Tu, Shih-Long)
研究員
- 國防醫學院生命科學研究所 博士
- 植物光感應及RNA剪接的分子機制
- tsl@gate.sinica.edu.tw
- tsl@as.edu.tw
- +886-2-2787-1045 (Lab: A321)
- +886-2-2787-1167 (Office: A342)
- Academia Sinica Archive
- ORCID
- Web of Science (WOS)
- Google Scholar
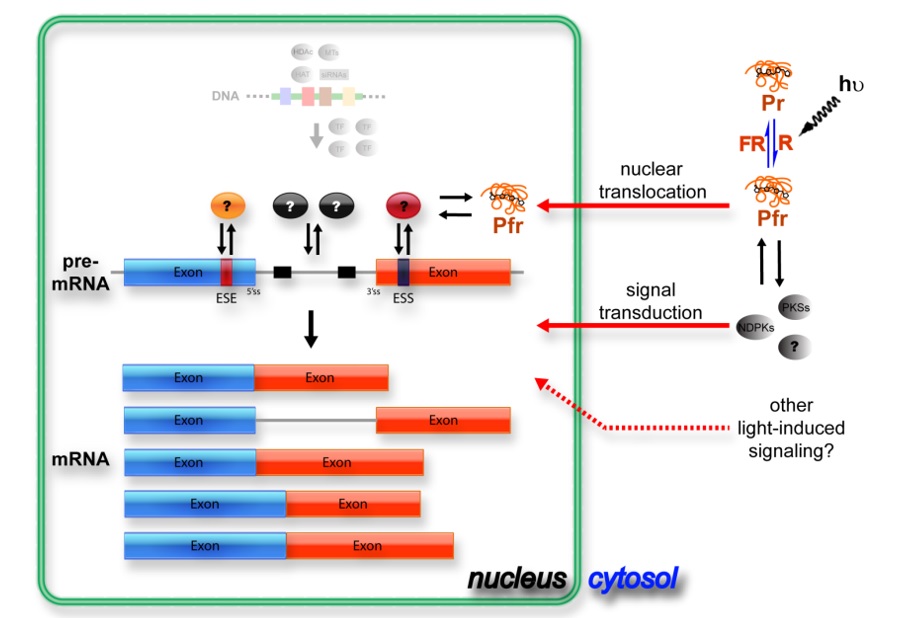
植物生長與分化容易受到環境變化影響,為了能因應環境的變化,植物已知可藉由訊息接收及傳遞,在不同層面來調控基因表現以控制生理及形態,目前相關研究相當多,但在訊息RNA剪接層面調控的機制了解卻很少。
替代性RNA剪接 (alternative splicing) 是真核生物中常見的機制,可以利用同樣的訊息RNA 前驅物 (pre-mRNA),在不同的剪接位進行剪接後,形成多條的訊息RNA,此機制大幅增加了轉錄體 (transcriptome) 及蛋白質體 (proteome) 的複雜度及多樣性。替代性RNA剪接可被剪接調控蛋白 (splicing regulator) 及調控序列 (regulatory cis element) 所影響,這幾年植物的轉錄體的相關研究雖已發現存在大量的替代性訊息RNA,然而對替代性RNA剪接的調控機制所知不多,其是否對植物抗逆境反應有幫助亦是未知。
我們近幾年利用系統生物學的研究方法,探討環境因子對植物體內替代性RNA剪接的影響。除了證實光線的確調控特定基因群的替代性RNA剪接,也發現光受器 (photoreceptor) 參與調控機制。目前我們利用功能性分析、生物化學及系統生物學的研究方法,探討光受器控制訊息RNA剪接的分子機制及其生理意義。希望這些研究可以幫助了解光受器調控訊息RNA剪接模式,以及此機制在植物的演化過程,最終利用此調控機制控制農作物的生長及分化。由於替代性剪接在植物不同生長階段都有參與調控,以開花時間的控制為例,如果更深入的探討與了解替代性剪接調控開花時間的機制,或許可以用此控制植物開花時間,目前研究團隊正就此方向進行研究。
- Chang, P., Hsieh, H.-Y., and Tu, S.-L. (2022). A novel U1 snRNP component RBP45d regulates temperature-responsive flowering in Arabidopsis thaliana. Plant Cell. 34, 834–851.
- Cheng, Y.-L., Hsieh, H.-Y., and Tu, S.-L. (2021). A new method to identify global targets of RNA-binding proteins in plants. bioRxiv. doi: 10.1101/2021.06.11.448000.
- Wang, C.-C., Hsieh, H.-Y., Hsieh, H-L. and Tu, S.-L. (2021). The chromatin adaptor PpMRG1 interacts with H3K36me3 and regulates light-responsive alternative splicing. Plant Physiol. 185, 1229-1241.
- Petrillo, E., Kalyna, M., Mandadi, K. K., Tu, S.-L. and Simpson, C. G. (2020) Editorial: Alternative splicing regulation in plants. Front. Plant Sci.11, 913.
- Shih, C.-J., Chen, H.-W., Hsieh, H.-Y., Chiu, F.-Y., Chen, Y.-R. and Tu, S.-L. (2019). Heterogeneous nuclear ribonucleoprotein H1 coordinates with phytochrome and the U1 snRNP complex to regulate alternative splicing in Physcomitrella patens. Plant Cell. 31, 2510-2524.
- Lin, B.-Y., Shih, C.-J., and Tu, S.-L. (2019). Phytochrome coordinates with a hnRNP to regulate alternative splicing via an exonic splicing silencer. Plant Physiol. 182, 243-254.
- Chang, Y.-M., Lin, H.-H., Liu, W.-Y., Yu, C.-P., Chen, H.-J., Wartini P. P., Kao, Y.-Y., Wu, Y.-H., Lin, J.-J., Lu, M.-Y., Tu, S.-L., Wu, S.-H., Shiu, S.-H., Ku, M.-S., and Li, W.-H. (2019). Comparative transcriptomics method to infer gene coexpression networks and its applications to maize and rice leaf transcriptomes. Proc. Natl. Acad. Sci. USA. 116, 3091-3099.
- Cheng, Y.-L. and Tu, S.-L. (2018). New insights of light-regulated alternative splicing. Plant. Cell. Physiol. Invited Review. 59, 1104-1110.
- C.-F., Yu, C.-P., Wu, Y.-H., Lu, M.-Y., Tu, S.-L., Wu, S.-H., Shiu, S.-H, Ku, M.-S., and Li, W.-H. (2017). Elevated auxin biosynthesis and transport underlie high vein density in C4 leaves. Proc. Natl. Acad. Sci. USA. 114, E6884-E6891.
- Huang, C.-F., Chang, Y.-M., Lin, J.-J., Yu, C.-P., Lin, H.-H., Liu, W.-Y., Yeh, S., Tu, S.-L., Wu, S.-H., Ku, M.-S.*, and Li, W.-H.* (2016). Insights into the regulation of C4 leaf development from comparative transcriptomic analysis. Curr. Opin. Plant Biol. 30, 1-10.
- Chang, C.-Y., Lin, W.-D., and Tu, S.-L. (2014). Genome-wide analysis of heat-sensitive alternative splicing in Physcomitrella patens. Plant Physiol. 165, 826-840.
- Wu, H.-P., Su, Y.-s., Chen, H.-C., Chen, Y.-R., Wu, C.-C., Lin, W.-D., and Tu, S.-L. (2014). Genome-wide analysis of light-regulated alternative splicing mediated by photoreceptors in Physcomitrella patens. Genome Biol. 15, R10.
- Chen, Y.-R., Su, Y.-s., and Tu, S.-L. (2012). Distinct phytochrome actions in non-vascular plants revealed by targeted inactivation of phytobilin biosynthesis. Proc. Natl. Acad. Sci. USA. 109, 8310-8315.
- Chiu, F.-Y., Chen, Y.-R., and Tu, S.-L. (2010). Electrostatic interaction of phytochromobilin synthase and ferredoxin for biosynthesis of phytochrome chromophore. J. Biol. Chem. 285, 5056-5065.
- Tu, S.-L., Chen, H.-C., Ku, L.-W. (2008). Mechanistic studies of the phytochromobilin synthase HY2 from Arabidopsis. J. Biol. Chem. 283, 27555-27564.


鄭有良 博士後研究員 yeoliang@gate.sinica.edu.tw

謝欣宇 研究助理 hsinyuh@gate.sinica.edu.tw

張平 博士班研究生 greenfavor@gate.sinica.edu.tw

林渤昀 博士班研究生 rogerbyl0704@gate.sinica.edu.tw

施玨如 博士班研究生 positivegloria@gate.sinica.edu.tw

王健彰 博士班研究生 taiwanod@gate.sinica.edu.tw
國際
- 2017 亞太光生物學會年輕學者獎 - 亞太光生物學會
國內
- 2022 傑出研究獎 - 國家科學及技術委員會
- 2013 年輕學者研究著作獎 - 中央研究院
- 2013 傑出學者養成計畫 - 國家科學委員會
- 2012 楊祥發院士傑出農業科學年輕學者獎 - 財團法人楊祥發紀念教育基金會
- 2010 前瞻計畫 - 中央研究院